
-

生物通官微
陪你抓住生命科技
跳动的脉搏
基于机器学习从蛋白质域特征预测细菌最适生长温度揭示热适应机制
【字体: 大 中 小 】 时间:2025年10月26日 来源:BMC Genomics 3.7
编辑推荐:
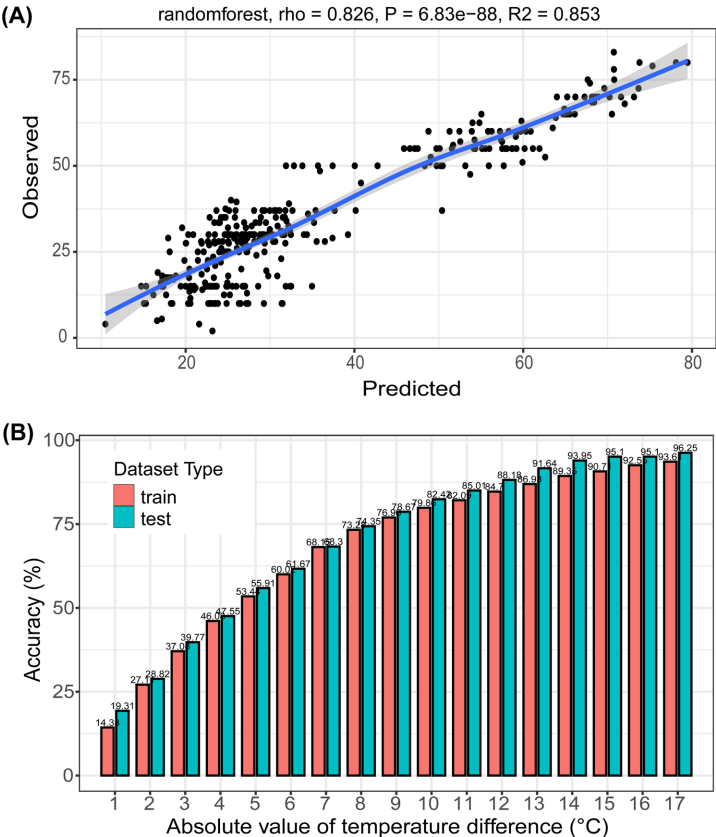
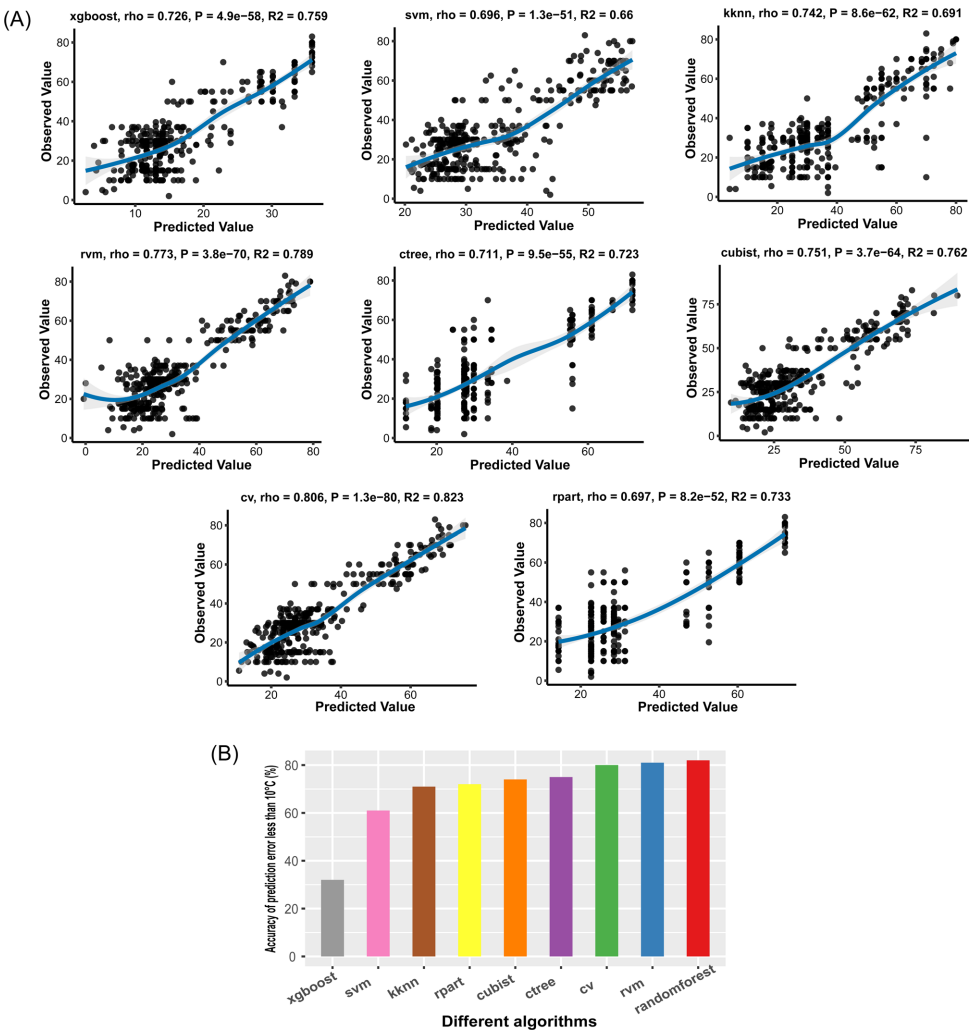
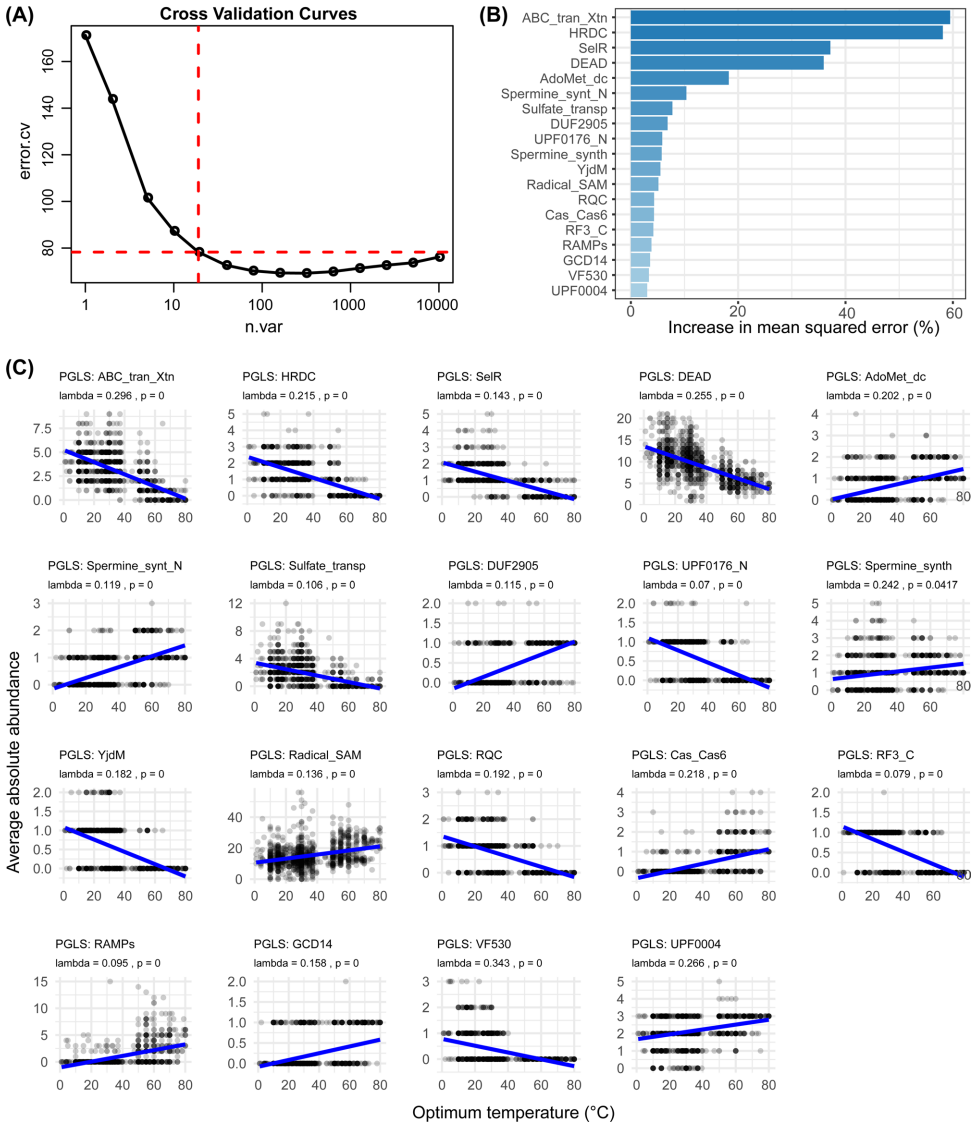
本研究针对绝大多数未培养微生物生理偏好未知的难题,开发了一种利用细菌基因组蛋白质域频率预测最适生长温度(OGT)的机器学习方法。研究人员基于1,498个基因组构建的随机森林模型预测精度显著,82.4%的预测误差在±10°C以内,为未培养微生物的定向培养提供了实用工具。模型分析揭示了与热适应相关的关键蛋白质域特征,多胺代谢、tRNA甲基转移酶家族和CRISPR-Cas系统的富集与较高OGT呈正相关,为理解细菌耐热性的分子机制提供了基因组证据。

 生物通微信公众号
生物通微信公众号